Kinase Substrate Profiling Array キナーゼアレイ
・スタンダードアレイにはセリン、スレオニン、チロシンキナーゼのリン酸化部位2100個が網羅的に配置されています.
・目的のキナーゼの基質特異性を網羅的にマッピングできます(図1、図2).
・複数のプロテインキナーゼの活性を測定し、比較するのに便利です.
・目的タンパク質の、リン酸化部位のマッピングにご利用いただけます.
・セルライセートや未知タンパク質から、新規キナーゼの探索が行えます(図3).
・リン酸化パターンを比較し、新規バイオマーカーの探索や、シグナルパスウェイの解析などに利用できます.
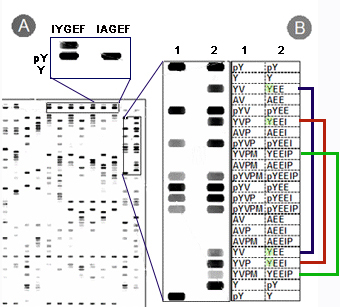
図1.Srcチロシン・キナーゼの基質特異性を測定した. (A)IYGEF配列のペプチドがポジティブコントロール(pY)と同程度にリン酸化されていることが分かります.一方チロシンをアラニンに置換したIAGEF 配列は全くリン酸化されておらず、ネガティブコントロールとして利用可能なことが分かります. (B)YVPM, YEEIP およびその置換配列を比較した. Src キナーゼのリン酸化活性はYEE(青線)およびYEEI(赤線)配列で高く、YEEIP(緑線)で弱いことが分かる. またYVP、YVPM は基質にならないことが分かる(列1).
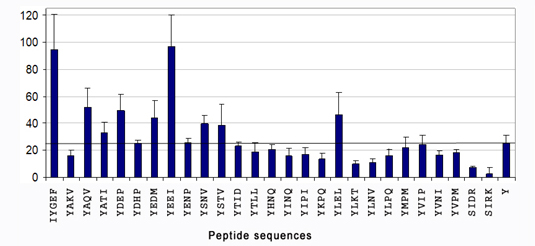
図2.Srcチロシン・キナーゼの基質特異性を測定した. 相対的リン酸化効率を計算すると、YEEI、IYGEF配列のリン酸化効率は90%以上であることが分かる.さらにSrcキナーゼは、E、D、G、Aなど、比較的小さいアミノ酸を+1位置に好むことが分かる.
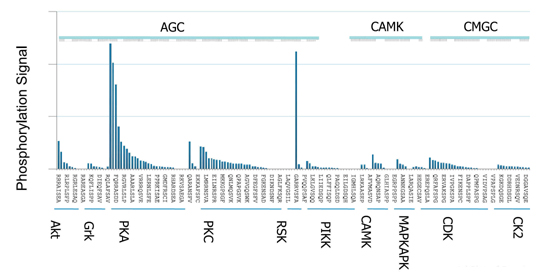
図3.未知のキナーゼの優先的結合パターンから、これがAGCファミリーに属するセリン・スレオニンキナーゼであり、PKAと類似の基質特異性を有することが分かる.